翟巍巍/马亮团队提出基于可解释深度学习模型的RNA速度解析新算法STEER
在复杂生命系统中,细胞状态会随着发育、组织重塑和疾病演化不断变化。RNA速度分析(RNA velocity)为从静态转录组数据中推断细胞状态演进趋势提供了重要手段。然而,在真实生物组织中,往往存在多种细胞动态过程并行发生、相互交织的情况,空间上相邻的细胞也可能遵循不同的动力学规律。现有RNA速度方法大多基于较为简化的单一动力学假设,难以有效区分复杂组织中的异质性信号,因此在解析复杂组织动态规律时仍面临挑战。
针对这一问题,2026年3月30日,中国科学院动物研究所翟巍巍/马亮团队在National Science Review发表题为“STEER: Decoupling kinetics with Spatial-Temporal Explainable Expert Model for RNA velocity inference”的研究论文,提出了一种面向复杂组织异质动力学解析的RNA速度推断新方法——STEER。该方法构建了融合时空信息与可解释混合专家机制的深度学习模型框架,突破了传统RNA速度方法对单一动力学系统的依赖,实现了对复杂组织中异质动力学模式的显式解耦。
STEER的核心思想是将“时空上下文建模”与“异质动力学解耦”相结合。一方面,方法综合利用细胞间的转录相似性与空间邻域关系,联合学习细胞的潜在时空状态表征;另一方面,通过可解释的混合专家机制,自适应地为不同细胞分配并拟合最优动力学子模型,从而区分和解耦混杂的动力学模式。基于这一设计,STEER不仅能够推断细胞状态的演进方向,还可联合估计潜在时间,以及细胞基因层面的转录、剪接和降解率等动力学参数。相较于传统方法,STEER进一步实现了对动力学机制差异的刻画,推动RNA速度分析由趋势描述迈向机制解析。
为系统验证STEER的有效性,作者在多种模拟数据和真实数据上进行了全面评估。结果表明,在不同细胞群体存在复杂动力学混合、且动力学规律并不一致的情况下,STEER仍能保持稳健而准确的推断性能,在速度方向恢复、潜在时间排序和动力学状态识别等方面均优于现有代表性方法。尤其值得注意的是,STEER能够在细胞表达差异尚不明显时,提前捕捉群体内部早期出现的动力学分歧。
在复杂空间组织研究中,STEER还展现出解析时空动态规律的独特优势。该方法无需预先对空间区域进行精细划分,便可分离相邻区域中不同甚至相反的动态过程。在小鼠母胎界面研究中,STEER揭示了胚胎侧与母体侧彼此协调、相互制衡的动态调控模式,为理解发育过程中的细胞状态时空演进规律及其免疫调节机制提供了新的计算视角。
综上,STEER针对复杂组织中多动力学过程混合、传统RNA速度方法难以准确建模的关键瓶颈,提出了一个兼具准确性、可解释性与泛化能力的新框架。该方法实现了异质动力学过程的显式解耦,并将空间信息、细胞状态演进与动力学参数建模统一起来,为发育生物学、组织稳态和疾病演化等研究提供了新的动态解析工具。随着单细胞与空间组学技术的持续发展,STEER有望在复杂生命系统时空动态机制研究中发挥更广泛的作用。
中国科学院动物研究所博士生刘志远为该论文第一作者,翟巍巍研究员与马亮副研究员为论文通讯作者。该研究得到中国科学院战略性先导专项,国家自然科学基金及国家重点研发计划等项目支持。
原文链接:https://doi.org/10.1093/nsr/nwag199
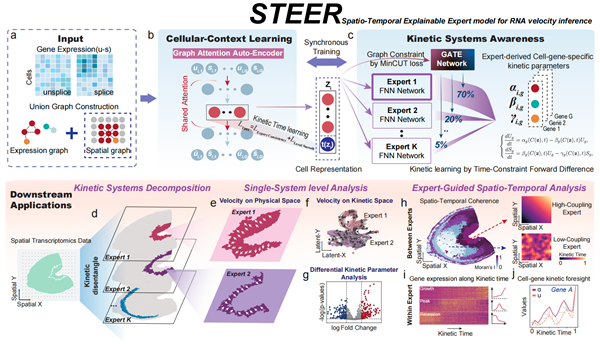
图1. STEER算法框架与下游应用
植物是生态系统中物质和能量循环的核心组成部分,并支撑整个生态系统的运转。在国家重点研发计划“区域生态产品核算技术方法与价值实现机制”项目的支持下,中国科学院动物研究所欧阳芳负责的 “典型农田生态系统...
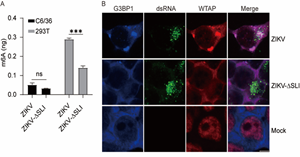
虫媒病毒如登革病毒、寨卡病毒在世界范围内流行,给人类健康和生物安全带来巨大挑战。这类病毒通过节肢动物媒介叮咬这一特殊方式在媒介-宿主之间进行传播。虫媒病毒必须在节肢动物媒介和脊椎动动物宿主之间交替感...

在人类活动空前扩张与全球气候变化叠加影响下,地球正经历严峻的生物多样性危机,全球约四分之一的物种正面临生存威胁。尽管世界各地持续推进濒危物种保育与再引入项目以扭转这一局面,但为什么有些物种能够成功...

